GWAS:拒绝假阳性之case和control数量比例严重失衡的解决方案(SAIGE模型的应用)
一、为什么要校正case和control数量比例不平衡情况
试问作为生信届人员,最怕的是什么,当然是统计结果不靠谱。统计结果不靠谱包括两方面:一个是假阴性,一个是假阳性。假阴性可以理解为白天鹅被误当成丑小鸭了,假阳性可以理解为一大堆青蛙,你不知道哪个才是你的真命天子。假阴性就罢了,最多让你错过发现真理的机会,但万一假阳性呢,你拿着一个看似完美的结果吭哧吭哧做实验验证,一年半载的周期下来,什么结果都验证不出来,岂不是坑了做实验的人。因此,我们就要在源头上,把这个不靠谱的统计结果杜绝出去。
上一篇文章什么!GWAS研究中case和control的比例是有讲究的?就讲到GWAS分析中,如果case和control数量比例失衡的话,会产出非常多的假阳性结果,而用SAIGE模型做GWAS分析可以校正这种数量比例不平衡的情况。下面具体讲讲怎么应用SAIGE模型。
二、怎么校正:SAIGE的下载和安装
1、下载SAIGE
此操作在Linux上进行,系统要求R-3.5.1, gcc >= 5.5.0, cmake 3.8.1
wget https://github.com/weizhouUMICH/SAIGE/blob/master/SAIGE_0.35.8.1_R_x86_64-pc-linux-gnu.tar.gz
2、安装SAIGE
R CMD INSTALL SAIGE_XX_R_x86_64-pc-linux-gnu.tar.gz
3、安装SAIGE所依赖的其他R包:Rcpp, RcppArmadillo, RcppParallel, data.table, SPAtest, RcppEigen, Matrix, methods, optparse
以下两个方法二选一:
如果是用conda的话,则用以下命令:
conda install -n r-env r-Rcpp #r-env是指conda下的R环境
conda install -n r-env r-RcppArmadillo
conda install -n r-env r-RcppParallel
conda install -n r-env r-SPAtest
conda install -n r-env r-RcppEigen
conda install -n r-env r-optparse
也可以进入R,用install.packages( )安装:
install.packages("Rcpp")
install.packages("RcppArmadillo")
install.packages("RcppParallel")
install.packages("SPAtest")
install.packages("RcppEigen")
install.packages("optparse")
三、怎么校正:SAIGE的分析、解读
1、第一步,计算NULL GLMM
1)计算NULL GLMM的命令:
Rscript step1_fitNULLGLMM.R \
--plinkFile=./input/plinkforGRM_1000samples_10kMarkers \
--phenoFile=./input/pheno_1000samples.txt \
--phenoCol=y \
--covarColList=x1,x2 \
--sampleIDColinphenoFile=IID \
--traitType=binary \
--outputPrefix=./output/example \
--nThreads=4 \
--LOCO=TRUE
plinkFile为plink的输入文件(bed, bim, fam格式)
phenoFile文件格式如下,第一列代表研究的表型,第二列及第N-1列代表协变量,最后一列IID为个体的ID号:

--phenoCol=y # 指定你要研究的表型列名,在本次例子中,指定y的表型分析。
--covarColList=x1,x2 #指定加入的协变量
--sampleIDColinphenoFile=IID #指定样本的ID
--traitType=binary #指定研究的表型的类型,binary指二分类,即case和control
--outputPrefix #生成文件的输出路径
2)输出文件的结果解读:
这个步骤会生成三个文件,分别为:example.rda、example.varianceRatio.txt、example_30markers.SAIGE.results.txt
第一个文件:example.rda,是一个model file
可以用R打开:
load("./output/example.rda")
names(modglmm)
modglmm$theta
第二个文件:example_30markers.SAIGE.results.txt,随意选取位点的关联分析结果
第三个文件:example.varianceRatio.txt
2、计算每个marker的SPA得分
1)计算每个marker的SNP得分命令:
Rscript step2_SPAtests.R \
--dosageFile=./input/dosage_10markers.txt \
--dosageFileNrowSkip=1 \
--dosageFileNcolSkip=6 \
--dosageFilecolnamesSkip=CHR,SNP,CM,POS,EFFECT_ALLELE,ALT_ALLELE \
--minMAF=0.0001 \
--sampleFile=./input/sampleIDindosage.txt \
--GMMATmodelFile=./output/example.rda \
--varianceRatioFile=./output/example.varianceRatio.txt \
--SAIGEOutputFile=./output/example.plainDosage.SAIGE.txt \
--numLinesOutput=2 \
--IsOutputAFinCaseCtrl=TRUE
dosage_10markers.txt的文件格式如下,类似于plink的ped格式,前六列分别为:CHR, SNP, CM, POS, COUNTED, ALT, 后面为个体的ID号:

sampleIDindosage.txt文件为样本ID名:

example.rda、example.varianceRatio.txt为第一步生成的两个文件。
2)输出文件的结果解读:
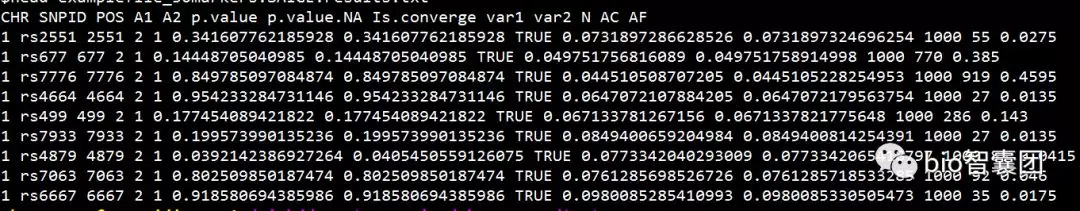
生成example.plainDosage.SAIGE.txt文件,其内容如下:

其中,P值(红框)即为我们校正case和control数量比例不平衡以后得到的GWAS结果,p.value.NA为不校正case和control数量不平衡的结果。
参数说明:
CHR: chromosome
POS: genome position
SNPID: variant ID
Allele1: Ref allele
Allele2: Alt allele
AC_Allele2: allele count of Alt allele
AF_Allele2: allele frequency of Alt allele
N: sample size
BETA: effect size
SE: standard error of BETA
Tstat: score statistic
p.value: p value with SPA applied
p.value.NA: p value when SPA is not applied
Is.SPA.converge: whether SPA is converged or not
varT: estimated variance of score statistic with sample related incorporated
varTstar: variance of score statistic without sample related incorporated
AF.Cases: allele frequency of allele 2 in cases (only for binary traits and if --IsOutputAFinCaseCtrl=TRUE)
AF.Controls: allele frequency of allele 2 in controls (only for binary traits and if --IsOutputAFinCaseCtrl=TRUE)
至此,校正GWAS分析中case和control数量比例严重失衡的工作就完成了。导师再也不用担心你给出一堆假阳性结果了。
GWAS:拒绝假阳性之case和control数量比例严重失衡的解决方案(SAIGE模型的应用)的更多相关文章
- GWAS研究中case和control的比例是有讲究的?
GWAS研究中,表型分两种.第一种是线性的表型,如果身高.体重.智力等:第二种是二元的表型,比如患病和未患病,即通常所说的case和control.对于表型是线性的样本来说,是不存在case和cont ...
- 在switch中的case语句中声明变量编译出错的解决方案
在switch中的case语句中声明变量编译的问题 先来看段代码,别管什么意思: : , j = ; ; i < ; i++) recive_phone[i] = msgbuf.text[i]; ...
- 全基因组关联分析学习资料(GWAS tutorial)
前言 很多人问我有没有关于全基因组关联分析(GWAS)原理的书籍或者文章推荐. 其实我个人觉得,做这个分析,先从跑流程开始,再去看原理. 为什么这么说呢,因为对于初学者来说,跑流程就像一个大黑洞,学习 ...
- GWAS | 全基因组关联分析 | Linkage disequilibrium (LD)连锁不平衡 | 曼哈顿图 Manhattan_plot | QQ_plot | haplotype phasing
现在GWAS已经属于比较古老的技术了,主要是碰到严重的瓶颈了,单纯的snp与表现的关联已经不够,需要具体的生物学解释,这些snp是如何具体导致疾病的发生的. 而且,大多数病找到的都不是个别显著的snp ...
- GWAS这十年 | 10 Years of GWAS Discovery: Biology, Function, and Translation
相关文章: A Unified Framework for Association Analysis with Multiple Related Phenotypes 太重要了,不得不单独拿出来分析一 ...
- 全基因组关联分析(Genome-Wide Association Study,GWAS)流程
全基因组关联分析流程: 一.准备plink文件 1.准备PED文件 PED文件有六列,六列内容如下: Family ID Individual ID Paternal ID Maternal ID S ...
- Oracle Applications Multiple Organizations Access Control for Custom Code
档 ID 420787.1 White Paper Oracle Applications Multiple Organizations Access Control for Custom Code ...
- if、else if 、else及switch...case使用小记(C#)
有时候编程编的久了,如果不停下来认真思考一下,即便是一些最基础的知识点,也可能让自己懵圈.其实,说到底还是打基础的时候没打牢,或者说自以为是地认为自己懂了,然后在打基础的时候就懒得思考懒得看了,结果就 ...
- JVM中可生成的最大Thread数量
最近想测试下Openfire下的最大并发数,需要开大量线程来模拟客户端.对于一个JVM实例到底能开多少个线程一直心存疑惑,所以打算实际测试下,简单google了把,找到影响线程数量的因素有下面几个: ...
随机推荐
- W3C 代码标准规范
W3C通过设立领域(Domains)和标准计划(Activities)来组织W3C的标准活动,围绕每个标准计划,会设立相关的W3C工作组织(包括工作组.社区组.商务组等).W3C会根据产业界的标准需求 ...
- 《JavaScript高级程序设计》笔记:函数表达式(七)
递归 function factorial(num){ if(num<=1){ return 1; }else { return num * arguments.callee(num-1); } ...
- 正确启动从GitHub上下载的vue项目:vueAdmin-template
先讲重点,后上相关资料: 遇到的问题:在启动从GitHub上下载的vue项目:vueAdmin-template 时报错:'webpack-dev-server' 不是内部或外部命令,也不是可运行的程 ...
- 转int啥啥啥的
1.String转int类型的话.需要用Double.valueof("这写String类型的数据").intValue(); 2.保留小数点: float scale = (fl ...
- Spring boot 发送邮件示例
最近的一个项目中用到了邮件发送,所以研究了一下.将其总结下来. 首先 登录邮箱 -->设置-->POP3/IMAP/SMTP/Exchange/CardDAV/CalDAV服务--> ...
- Maven deploy部署jar包到远程私仓
Maven deploy部署jar包到远程私仓 maven deploy介绍 maven中的仓库分为两种,snapshot快照仓库和release发布仓库.snapshot快照仓库用于保存开发过程中的 ...
- 该用Python还是SQL?4个案例教你节省时间
在数据分析行业,对数据提出的每一个问题都可以用多种潜在的语言和工具包来回答.每种语言都有其优势,它们之间也存在着不同的区别.不能否认的是,有些操作用Python执行起来要比SQL更加高效.这篇文章分享 ...
- 利用ZYNQ SOC快速打开算法验证通路(6)——利用AXI总线实时配置sysGen子系统
利用ZYNQ验证算法的一大优势在于,可以在上位机发送指令借助CPU的控制能力和C语言易开发特点,实时配置算法模块的工作模式.参数等对来对其算法模块性能进行全面的评估.最重要的是无需重新综合硬件模块. ...
- win7下怎么安装IIS
工具/原料 win7旗舰版系统 笔记本一台 WIN7下怎么安装iis教程: 点击开始→控制面板,然后再点击程序和功能,勿点击卸载程序,否则到不了目标系统界面. 然后在程序和功能下面,点击打开和关闭wi ...
- IBM developer:Setting up the Kafka plugin for Ranger
Follow these steps to enable and configure the Kafka plugin for Ranger. Before you begin The default ...
