(数据科学学习手札11)K-means聚类法的原理简介&Python与R实现
kmeans法(K均值法)是麦奎因提出的,这种算法的基本思想是将每一个样本分配给最靠近中心(均值)的类中,具体的算法至少包括以下三个步骤:
1.将所有的样品分成k个初始类;
2.通过欧氏距离将某个样品划入离中心最近的类中,并对获得样品与失去样品的类重新计算中心坐标;
3.重复步骤2,直到所有的样品都不能在分类为止
kmeans法与系统聚类法一样,都是以距离的远近亲疏为标准进行聚类的。但是两者的不同之处也很明显:系统聚类对不同的类数产生一系列的聚类结果,而K均值法只能产生指定类数的聚类结果。具体类数的确定,离不开实践经验的积累。有时也可借助系统聚类法,以一部分样本(简单随机抽样)为对象进行聚类,其结果作为K均值法确定类数的参考。
kmeans算法以k为参数,把n个对象分为k个聚类,以使聚类内具有较高的相似度,而聚类间的相似度较低。相似度的计算是根据一个聚类中对象的均值来进行的。kmeans算法的处理流程如下:随机地选择k个对象,每个对象初始地代表了一个簇的平均值或中心;对剩余的每个对象,根据其与各个聚类中心的距离将其赋给最近的簇;重新计算每个簇的平均值作为聚类中心进行聚类。这个过程不断重复,直到准则函数收敛,得到最终需要的k个类,算法结束;准则函数通常采用最小平方误差准则:
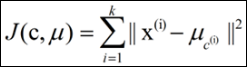
关于k具体数值的选择,在实际工作大多数是根据需求来主观定(如衣服应该设计几种尺码),在这方面能够较直观的求出最优k的方法是肘部法则,它是绘制出不同k值下聚类结果的代价函数,选择最大拐点作为最优k值。
而在Python与R中都各自有实现K-means聚类的方法,下面一一介绍:
Python
Python的第三方包中可以用来做Kmeans聚类的包有很多,本文主要介绍Scipy和sklearn中各自集成的方法;
1.利用Scipy.cluster中的K-means聚类方法
scipy.cluster.vq中的kmeans方法为kmeans2(data,n),data为输入的样本数据矩阵,样本x变量的形式;n为设定的聚类数。
这里我们分别生成5个100x10的高维正态分布随机数,标准差均为0.8,均值分别为1,2,3,4,5,并将其拼接为500x10的矩阵,并按行打乱顺序进行聚类,鉴于维度为10大于2,为了在二维平面上进行可视化,我们使用sklearn包中的降维方法TSNE来对样本数据进行10维至2维的降维以可视化,具体代码如下:
import numpy as np
from scipy.cluster.vq import *
import matplotlib.pyplot as plt
from sklearn.manifold import TSNE '''生成示例数据'''
set1 = np.random.normal(1,0.8,(100,10))
set2 = np.random.normal(2,0.8,(100,10))
set3 = np.random.normal(3,0.8,(100,10))
set4 = np.random.normal(4,0.8,(100,10))
set5 = np.random.normal(5,0.8,(100,10)) '''将两个列数相同的矩阵上下拼接,类似R中的rbind()'''
data = np.concatenate((set1,set2,set3,set4,set5)) '''按行将所有样本打乱顺序'''
np.random.shuffle(data) '''进行kmeans聚类'''
res, idx = kmeans2(data,5) '''为不同类的样本点分配不同的颜色'''
colors = ([([0.4,1,0.4],[1,0.4,0.4],[0.4,0.4,0.4],[0.4,0.4,1.0],[1.0,1.0,1.0])[i] for i in idx]) '''对样本数据进行降维以进行可视化'''
data_TSNE = TSNE(learning_rate=100).fit_transform(data) '''绘制所有样本点(已通过聚类结果修改对应颜色)'''
plt.scatter(data_TSNE[:,0],data_TSNE[:,1],c=colors,s=12)
plt.title('K-means Cluster')
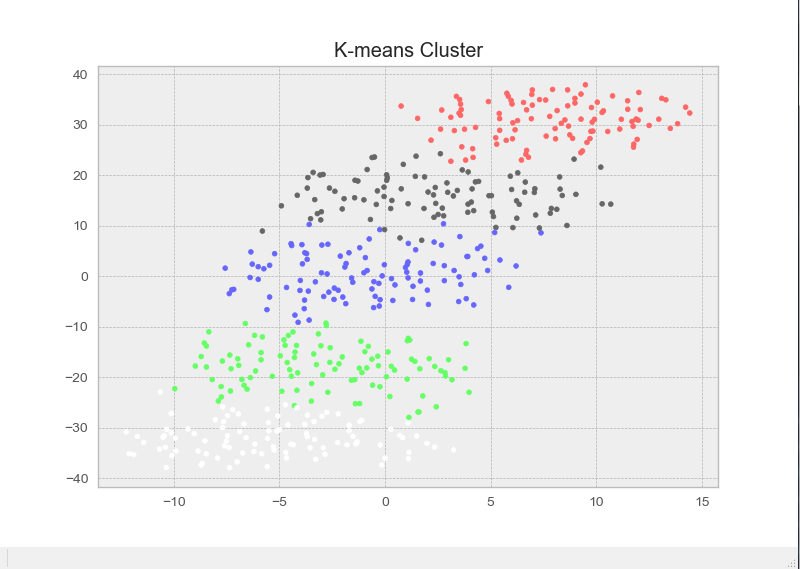
可以看出,我们通过kmeans顺利的将这些数据分到五个类中(有一类颜色为白色),足以见得kmeans在对常规数据的聚合上效果较好,下面我们假装事先不知道样本数据准确的分类数目,利用肘部法则来选取最优k值:
import numpy as np
from scipy.cluster.vq import *
import matplotlib.pyplot as plt
from sklearn.manifold import TSNE
from scipy.spatial.distance import cdist
from matplotlib.ticker import MultipleLocator xmajorLocator = MultipleLocator(1)
'''生成示例数据'''
set1 = np.random.normal(1,0.5,(100,10))
set2 = np.random.normal(8,0.5,(100,10)) '''将两个列数相同的矩阵上下拼接,类似R中的rbind()'''
data = np.concatenate((set1,set2)) '''按行将所有样本打乱顺序'''
np.random.shuffle(data) K = range(1,5)
cost = []
'''记录代价变化情况'''
for k in K:
res, idx = kmeans2(data, k)
cost.append(sum(np.min(cdist(data,res,'euclidean'),axis=1))/data.shape[0]) '''绘制代价变化图'''
ax = plt.subplot(111)
plt.plot(K,cost)
ax.xaxis.set_major_locator(xmajorLocator)
plt.title('cost change')

可以看出,在k=2的时候,我们找到了对应的‘肘部’,这与真实的类数相同,下面我们进行真实类数较多时的k值选择:
import numpy as np
from scipy.cluster.vq import *
import matplotlib.pyplot as plt
from sklearn.manifold import TSNE
from scipy.spatial.distance import cdist
from matplotlib.ticker import MultipleLocator
from matplotlib import style xmajorLocator = MultipleLocator(1)
'''生成示例数据'''
set1 = np.random.normal(1,1,(100,10))
set3 = np.random.normal(2,1,(100,10))
set4 = np.random.normal(3,1,(100,10))
set6 = np.random.normal(4,1,(100,10)) '''将两个列数相同的矩阵上下拼接,类似R中的rbind()'''
data = np.concatenate((set1,set3,set4,set6)) '''按行将所有样本打乱顺序'''
np.random.shuffle(data) K = range(2,6)
cost = []
'''记录代价变化情况'''
plt.figure(figsize=(12,8))
for k in K:
res, idx = kmeans2(data, k)
'''为不同类的样本点分配不同的颜色'''
colors = ([['red','blue','black','yellow','green'][i] for i in idx]) '''对样本数据进行降维以进行可视化'''
data_TSNE = TSNE(learning_rate=100).fit_transform(data) '''绘制所有样本点(已通过聚类结果修改对应颜色)'''
plt.subplot(219+k)
style.use('bmh')
plt.scatter(data_TSNE[:, 0], data_TSNE[:, 1], c=colors, s=12)
plt.title('K-means Cluster of {}'.format(str(k)))
cost.append(sum(np.min(cdist(data,res,'euclidean'),axis=1))/data.shape[0]) '''绘制代价变化图'''
ax = plt.subplot(111)
plt.plot(K,cost)
ax.xaxis.set_major_locator(xmajorLocator)
plt.title('cost change')
以下是不同类数时的聚类图以及代价函数变化图:
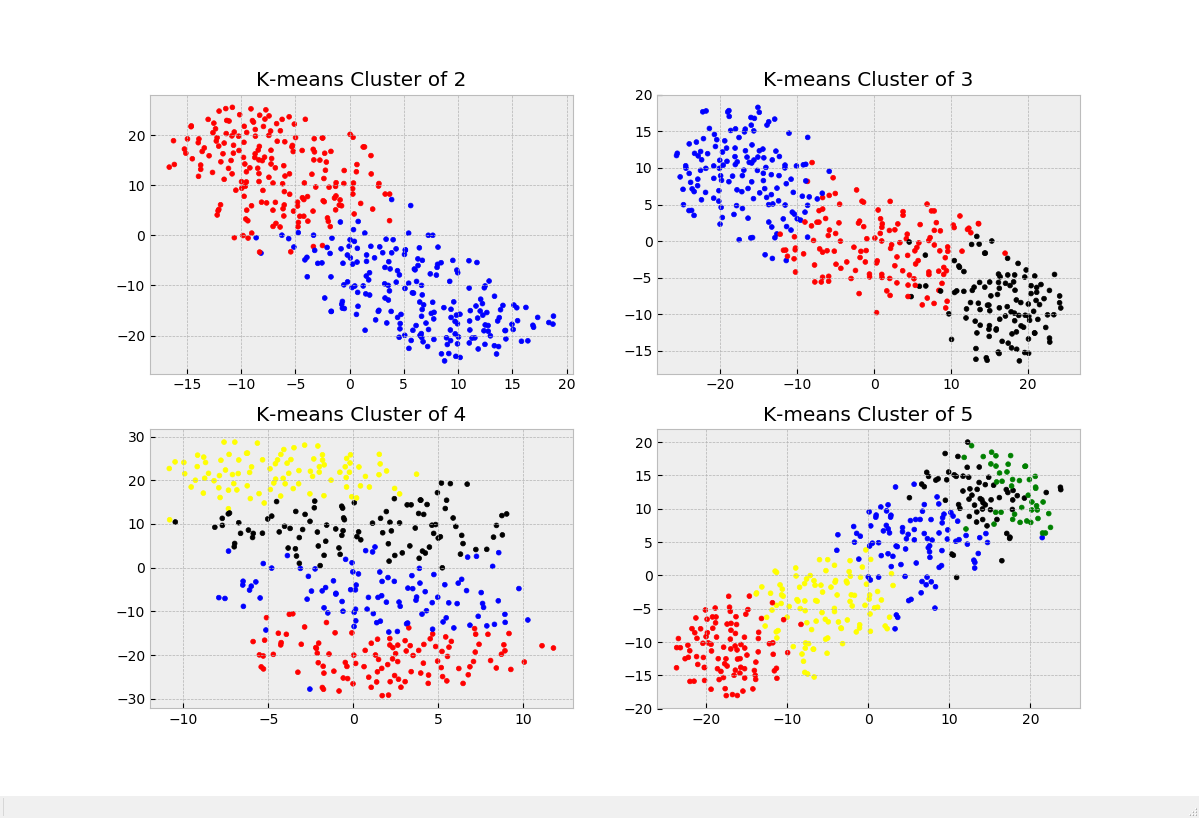
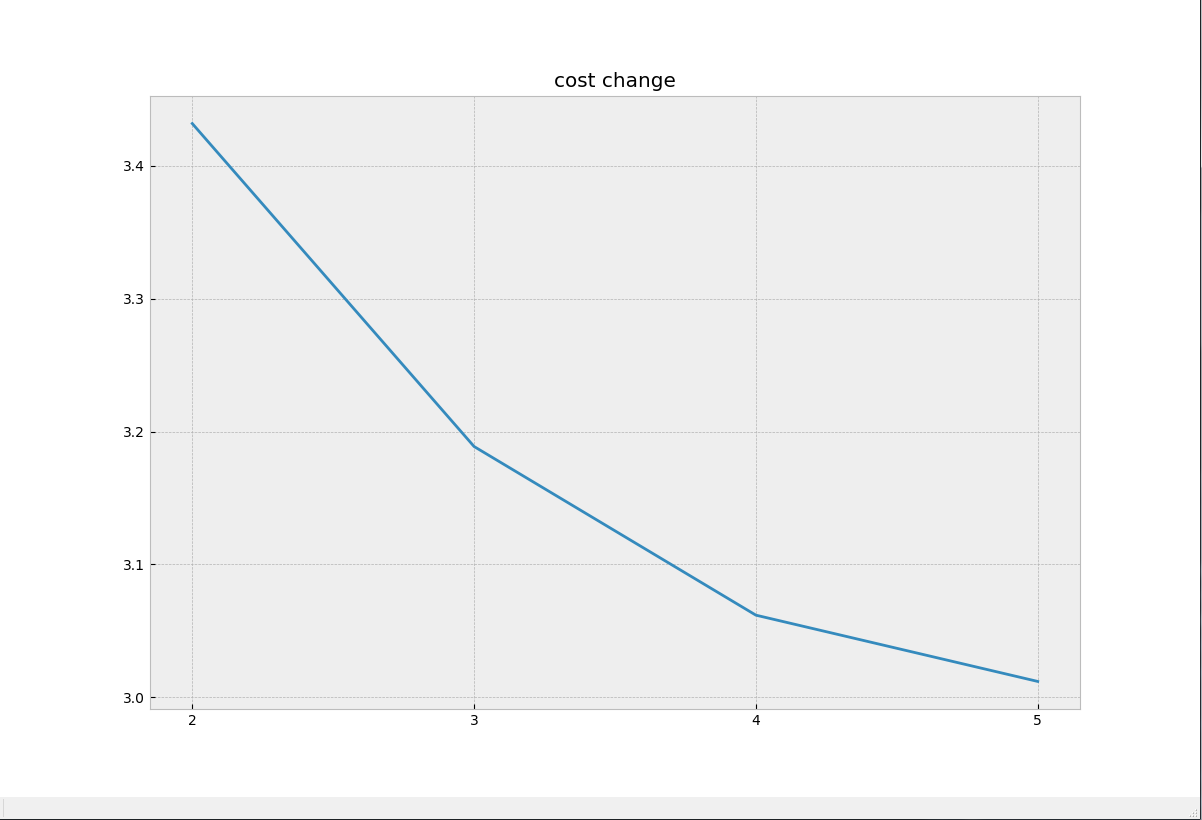
可以看出,在各个类的真实分类较为均匀的时候,肘部法则就失去了意义,因为这时我们无法分辨代价函数的减小是得益于k选的好还是k值的增大。
2.利用sklearn中的方法进行K-means聚类
作为Python中赫赫大名的机器学习包,sklearn中封装的kmeans算法也非常成熟稳定,sklearn.cluster中的KMeans(n_clusters=n,init,n_jobs).fit(data):n_clusters表示设定的聚类个数k,默认为8;init表示初始选择簇中心的方法,有‘kmeans++’与‘random’;n_jobs用来控制线程,-1为CPU全开
from sklearn.manifold import TSNE
from sklearn.cluster import KMeans
import numpy as np
import matplotlib.pyplot as plt '''生成聚类样本数据'''
set1 = np.random.normal(1,0.7,(100,10))
set2 = np.random.normal(2,0.7,(100,10))
set3 = np.random.normal(3,0.7,(100,10)) data = np.concatenate((set1,set2,set3))
np.random.shuffle(data) '''生成可视化需要的2维降维数据'''
data_tsne = TSNE(learning_rate=100).fit_transform(data)
colors = ['b', 'g', 'r', 'y', 'k', 'c', 'm', 'chartreuse']
plt.figure(figsize=(12,8)) '''对不同的k值设定进行聚类并绘图'''
for i in range(2,8):
kmeans_model = KMeans(n_clusters=i,init='random',n_jobs=-1).fit(data)#sklearn中的kmeans方法
color = [colors[k] for k in kmeans_model.labels_]
plt.subplot(229+i)
plt.scatter(data_tsne[:,0],data_tsne[:,1],color=color)
plt.title('{} clusters'.format(str(i)))
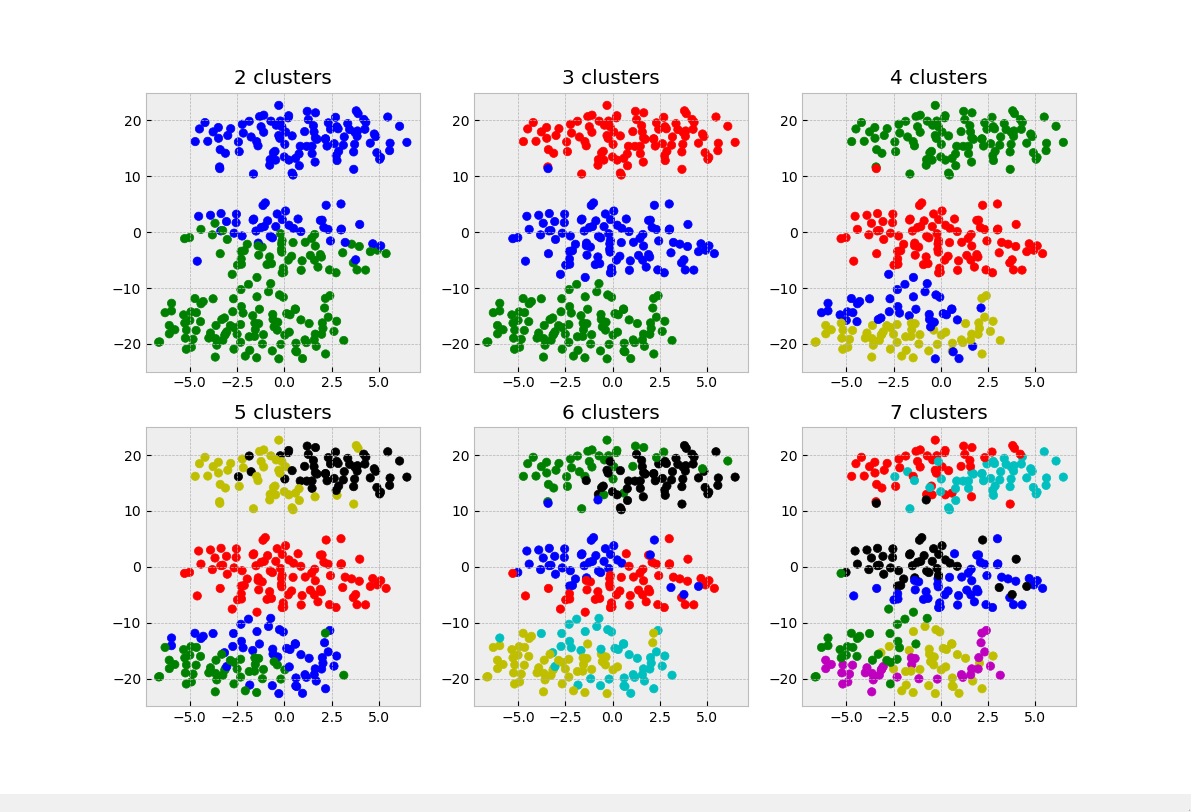
从主观上看,k=3时效果最好,这也与真实样本的分布类数一致。
R
在R中做K-means聚类就非常轻松了,至少不像Python那样需要安装第三方包,在R中自带的kmeans(data,centers,iter.max)可以直接用来做K-means聚类,其中data代表输入的待聚类样本,形式为样本x变量,centers代表设定的聚类簇数量,iter.max代表算法进行迭代的最大次数,一般比较正常的数据集不会消耗太多次迭代;下面针对低维样本与高维样本分别进行K-means聚类:
一、低维
这里我们生成两类正态分布随机数据,分别是0均值0.7标准差,和3均值0.7标准差,将其拼接在一起,共10000x2的矩阵作为输入变量,设置k分别等于2,3,4,5来看看聚类结果的不同:
#kmeans聚类法
library(RColorBrewer) data1 <- matrix(rnorm(10000,mean=0,sd=0.7),ncol=2)
data2 <- matrix(rnorm(10000,mean=5,sd=0.7),ncol=2)
data <- rbind(data1,data2) pch1 <- rep('',5000)
pch2 <- rep('',5000)
#设置颜色
cols<-brewer.pal(n=5,name="Set1")
par(mfrow=c(2,2))
for(i in 2:5){
cl <- kmeans(data,centers = i,iter.max = 10)
plot(data,col=cols[cl$cluster],pch=c(pch1,pch2),cex=0.9)
title('K-means Result')
points(cl$centers,col='yellow',pch='x',cex=1.5)
}
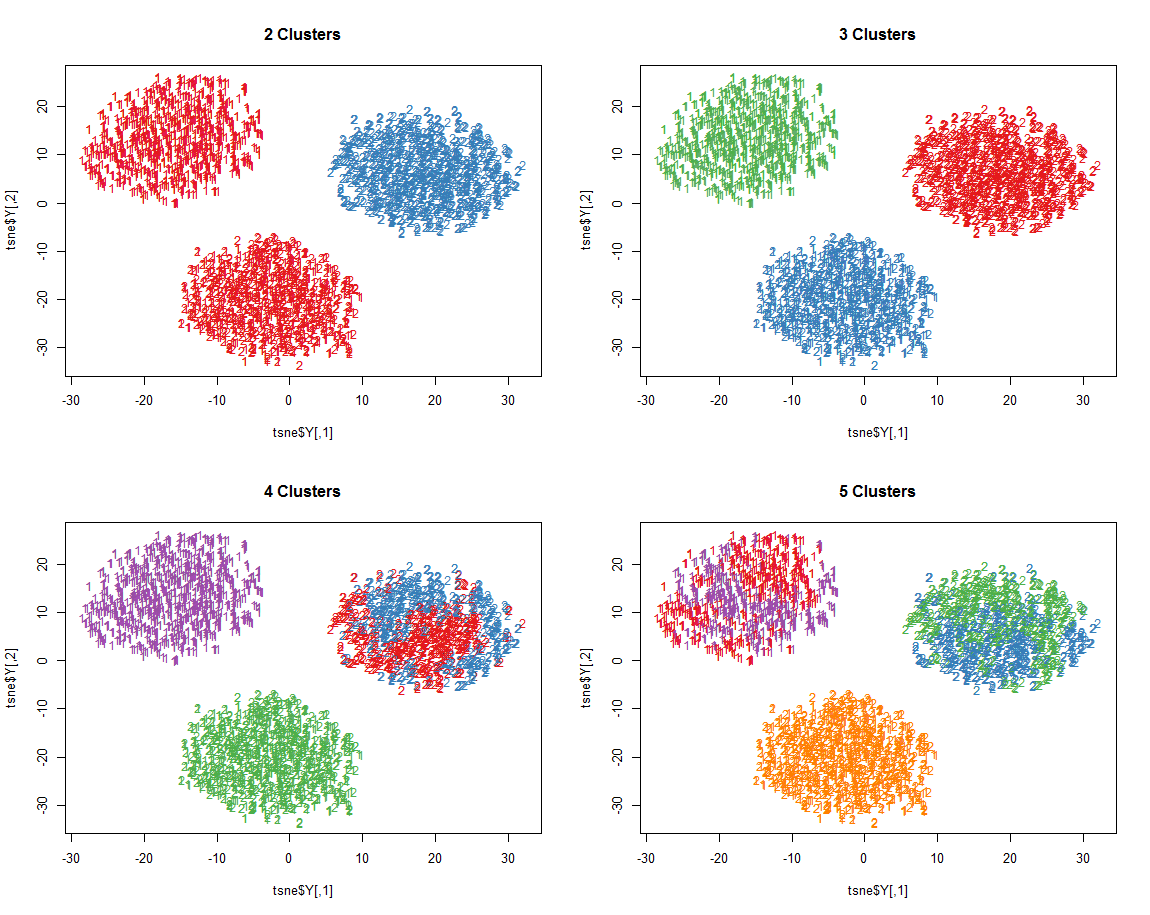
聚类结果可视化如下:

二、高维
当样本数据的维度远远大于3时,就需要对其进行降维至2维以进行可视化,和前面所说的TSNE类似,R中也有同样功能的降维包Rtsne,下面我们就对一个维度较高的(10维)的样本数据集进行聚类及降维可视化:
#kmeans聚类法
library(Rtsne)
library(RColorBrewer) data1 <- matrix(rnorm(10000,mean=0,sd=0.7),ncol=10)
data2 <- matrix(rnorm(10000,mean=5,sd=0.7),ncol=10)
data3 <- matrix(rnorm(10000,mean=10,sd=0.7),ncol=10)
data <- rbind(data1,data2,data3) #设置对应样本的点型
pch1 <- rep('',length(data[,1])*0.5)
pch2 <- rep('',length(data[,1])*0.5)
pch3 <- rep('',length(data[,1])*0.5)
#设置颜色
cols<-brewer.pal(n=5,name="Set1")
#数据的降维(降至2维)
tsne <- Rtsne(data)
#自定义代价函数计算函数
Mycost <- function(data,centers_){
l <- length(data[,1])
d <- matrix(0,nrow=l,ncol=length(centers_[,1]))
for(i in 1:l){
for(j in 1:length(centers_[,1])){
dd <- 0
for(k in 1:length(data[1,])){
dd <- dd + (data[i,k]-centers_[j,k])^2
}
d[i,j] <- sqrt(dd)
}
}
mindist <- apply(d,1,min)
return(sum(mindist))
}
opar <- par(no.readonly = TRUE)
#初始化代价函数记录向量
zb <- c()
par(mfrow=c(2,2))
#分别根据不同的k进行聚类并可视化
for(i in 2:5){
cl <- kmeans(data,centers = i,iter.max = 10)
plot(tsne$Y,col=cols[cl$cluster],pch=c(pch1,pch2,pch3),cex=0.9)
title(paste(as.character(i),'Clusters'))
zb[i-1] <- Mycost(data,cl$centers)
}
par(opar)
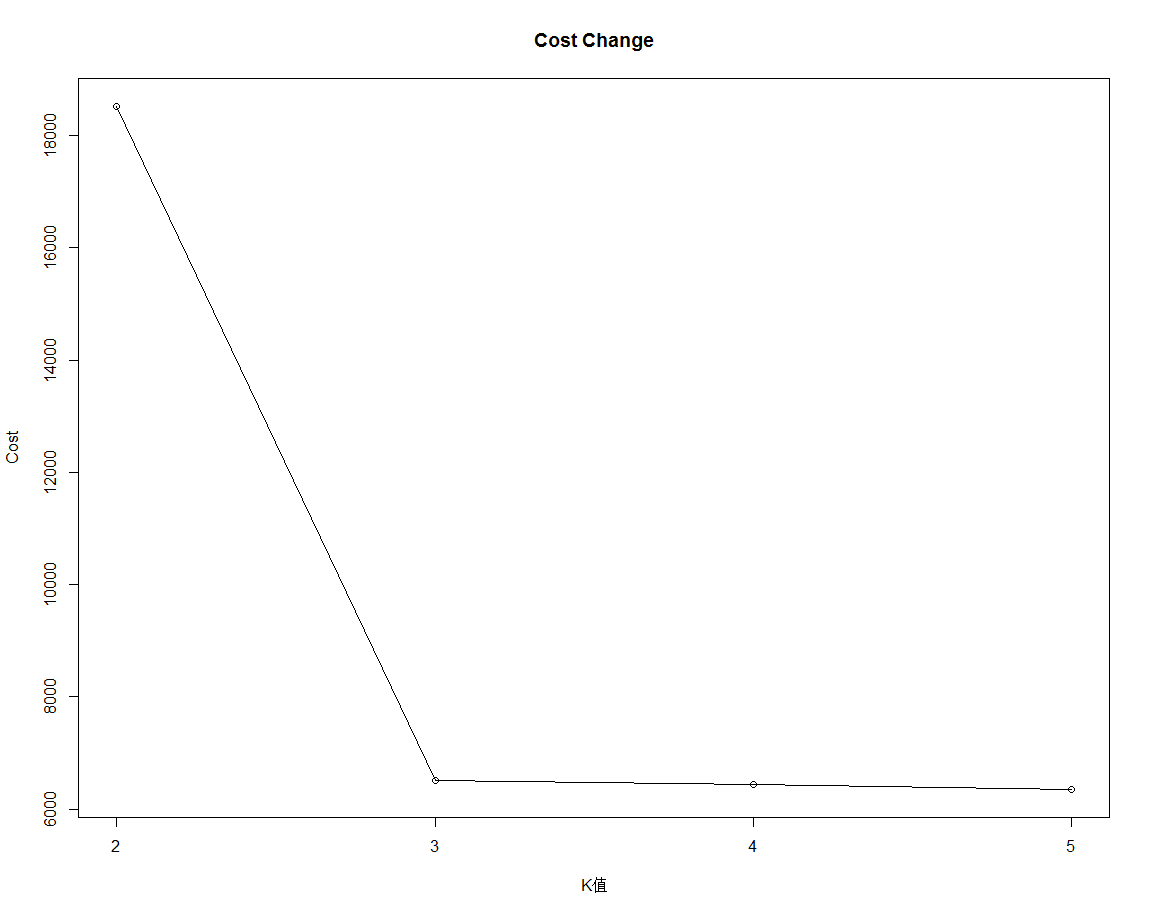
绘制代价函数变化图:
#绘制代价函数随k的增加变化情况
plot(2:5,zb,type='o',xaxt='n',xlab='K值',ylab='Cost')
axis(1,at=seq(2,5,1))
title('Cost Change')
总结:Python与R在K-means上各有各的有点,Python方法众多,运算速度快,只是一些细节不够到位;R非常专业,过程也很简洁,只是在运算速度上稍逊一筹,如果让笔者以后实际工作选择的话,我还是更倾向于R,因为其kmeans函数非常“听话”,严格按照设置的类去分,虽然有时会出现一些不合理的地方;Python则没那么“听话”,有些时候,如果被它的算法内部判定为不可再分,则它会在设定的K值下产生一些任性的空类。
如有发现笔者写错的地方,望多多指出。
(数据科学学习手札11)K-means聚类法的原理简介&Python与R实现的更多相关文章
- (数据科学学习手札18)二次判别分析的原理简介&Python与R实现
上一篇我们介绍了Fisher线性判别分析的原理及实现,而在判别分析中还有一个很重要的分支叫做二次判别,本文就对二次判别进行介绍: 二次判别属于距离判别法中的内容,以两总体距离判别法为例,对总体G1,, ...
- (数据科学学习手札14)Mean-Shift聚类法简单介绍及Python实现
不管之前介绍的K-means还是K-medoids聚类,都得事先确定聚类簇的个数,而且肘部法则也并不是万能的,总会遇到难以抉择的情况,而本篇将要介绍的Mean-Shift聚类法就可以自动确定k的个数, ...
- (数据科学学习手札08)系统聚类法的Python源码实现(与Python,R自带方法进行比较)
聚类分析是数据挖掘方法中应用非常广泛的一项,而聚类分析根据其大体方法的不同又分为系统聚类和快速聚类,其中系统聚类的优点是可以很直观的得到聚类数不同时具体类中包括了哪些样本,而Python和R中都有直接 ...
- (数据科学学习手札16)K-modes聚类法的简介&Python与R的实现
我们之前经常提起的K-means算法虽然比较经典,但其有不少的局限,为了改变K-means对异常值的敏感情况,我们介绍了K-medoids算法,而为了解决K-means只能处理数值型数据的情况,本篇便 ...
- (数据科学学习手札10)系统聚类实战(基于R)
上一篇我们较为系统地介绍了Python与R在系统聚类上的方法和不同,明白人都能看出来用R进行系统聚类比Python要方便不少,但是光介绍方法是没用的,要经过实战来强化学习的过程,本文就基于R对2016 ...
- (数据科学学习手札13)K-medoids聚类算法原理简介&Python与R的实现
前几篇我们较为详细地介绍了K-means聚类法的实现方法和具体实战,这种方法虽然快速高效,是大规模数据聚类分析中首选的方法,但是它也有一些短板,比如在数据集中有脏数据时,由于其对每一个类的准则函数为平 ...
- (数据科学学习手札12)K-means聚类实战(基于R)
上一篇我们详细介绍了普通的K-means聚类法在Python和R中各自的实现方法,本篇便以实际工作中遇到的数据集为例进行实战说明. 数据说明: 本次实战样本数据集来自浪潮集团提供的美团的商家信息,因涉 ...
- (数据科学学习手札09)系统聚类算法Python与R的比较
上一篇笔者以自己编写代码的方式实现了重心法下的系统聚类(又称层次聚类)算法,通过与Scipy和R中各自自带的系统聚类方法进行比较,显然这些权威的快捷方法更为高效,那么本篇就系统地介绍一下Python与 ...
- (数据科学学习手札30)朴素贝叶斯分类器的原理详解&Python与R实现
一.简介 要介绍朴素贝叶斯(naive bayes)分类器,就不得不先介绍贝叶斯决策论的相关理论: 贝叶斯决策论(bayesian decision theory)是概率框架下实施决策的基本方法.对分 ...
随机推荐
- Struts2的学习-通配符和session对象
一. 取得session 3种方法1.context.getSession() -->>Map对象 2.HttpServletRequest request =(HttpServletRe ...
- POJ-3104 Drying---二分答案判断是否可行
题目链接: https://cn.vjudge.net/problem/POJ-3104 题目大意: 有一些衣服,每件衣服有一定水量,有一个烘干机,每次可以烘一件衣服,每分钟可以烘掉k滴水.每件衣服每 ...
- LA 4731 蜂窝网络
题目链接:https://vjudge.net/problem/UVALive-4731 题意: n 个 数,分成 w 组,求整个区间的数学期望的最小值: 一个区间的数学期望公式给出:一个区间的和 * ...
- MYSQL5.7.15安装步骤
下载完成之后双击安装: 接下来一路next (出现的问题) 在我第一次安装myslq过程中,上图中的mysql server failed ,这是因为电脑环境需要升级一个插件,Visual C++ 2 ...
- 【luogu P3384 树链剖分】 模板
题目链接:https://www.luogu.org/problemnew/show/P3384 诶又给自己留了个坑..不想写线段树一大理由之前的模板变量名太长 #include <cstdio ...
- 【luogu P3627 [APIO2009]抢掠计划】 题解
题目链接:https://www.luogu.org/problemnew/show/P3627 把点权转化到边权上去. #include <stack> #include <que ...
- Android学习笔记_76_Android ProgressBar 进度条
android 进度条的样式 例1:(默认样式(中等圆形))Xml代码 <ProgressBar android:id="@+id/progressBar1" ...
- python logging—模块
python logging模块 python logging提供了标准的日志接口,python logging日志分为5个等级: debug(), info(), warning(), error( ...
- Restframework中的Request
1.介绍 该篇博客主要介绍restframework内置的Request类,它扩展了Django中的Request类,实现了很多方便的功能--如请求数据解析和认证等. 如: 在APIView中封装的r ...
- JavaScript 笔记总结
一.js的简介 1.js是什么 js是可以嵌入到html中,是 基于对象 和 事件驱动 的 脚本语言 特点: (1)交互性 (2)安全性:js不能访问本地磁盘 (3)跨平台:浏览器中都具备js解析器 ...
